2b-RAD的十大技术应用总结(中篇)
2b-RAD,革新的划时代简化基因组技术,以其高可重复性、全库测序、测序深度均一、标签独立性好等各项优势,不仅技术方法刊登在《Nature Methods》上,也广泛受到研究工作者的好评,近年来陆续发表多篇文献在各大期刊上。
我们作为发明方独家授权合作的专业技术服务商,今天将继续带来『亲缘关系、全基因组选择育种、细胞突变检测』的分享。
应用4:亲缘关系
研究背景:随着基因组时代的到来,研究者可以通过全基因组测序研究物种间的进化关系。但是对于经济价值不高、基因组过大的物种来说,这种方法是不合适的。简化基因组技术,2b-RAD不但经济划算,而且可以在基因组层面提供很多有价值的信息,可应用于分子标记开发、群体遗传、甚至进化研究。
研究内容:美国研究人员采用2b-RAD技术对21种果蝇进行了系统发生关系的阐述,研究结果与当前公认的果蝇进化关系相吻合。表明2b-RAD技术适用于进行高准确度系统发生树的构建,加快比较基因组的研究,尤其是那些没有基因组信息的物种。

图1 21种果蝇的基因组信息
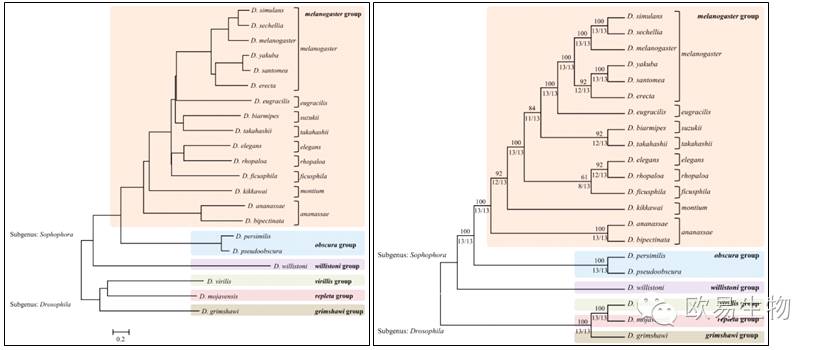
图2 由内切酶AloI数据构建的系统进化树
图3 综合13种内切酶数据的拓扑结构
研究策略
实验材料:从数据库获得21种果蝇的基因组信息(图1)。
实验方法:13种IIB型限制性内切酶对21种果蝇基因组进行电子酶切。
分析方法:每种内切酶酶切后的标签,进行两两比较,得到两种果蝇的共有标签。根据共有标签,计算遗传距离,构建系统发育树。
实验材料:从数据库获得21种果蝇的基因组信息(图1)。
实验方法:13种IIB型限制性内切酶对21种果蝇基因组进行电子酶切。
分析方法:每种内切酶酶切后的标签,进行两两比较,得到两种果蝇的共有标签。根据共有标签,计算遗传距离,构建系统发育树。
研究结果
一种IIB型限制性内切酶产生的2b-RADtag,13种IIB型限制性内切酶产生的2b-RADtag分别进行果蝇系统发生树的构建,其拓扑结构高度一致(图2、3)。
参考文献
Seetharam A S, Stuart G W. Whole genomephylogeny for 21 Drosophila species using predicted 2b-RAD fragments[J]. PeerJ, 2013, 1: e226. (IF: 2.112)
应用5:全基因组选择育种
研究背景:基因组选择(GenomicSelection, GS)利用覆盖整个基因组的SNP标记估计基因组育种值(GenomicEstimated Breeding Values, GEBV),可以减少代数间隔或增加选择强度,加速育种效率。
研究内容:中国海洋大学包振民教授课题组首次将2b-RAD技术应用到扇贝的基因组选择育种。通过6种统计模型分析模拟数据和实验数据,表明在农业育种方面,2b-RAD是一种理想的可应用于基因组选择的基因分型平台。
研究策略
育种群体模拟:3个模拟群体,第一个模拟群体是从繁育1000代的群体中随机挑选100个父本和100个母本交配,每次交配得到20个子代G1,重复此过程得到G2。第二个模拟群体由20个full-sib家系组成,每个家系包括50个子代,这50个子代是从繁育1000代的群体中随机挑选10个父本和10个母本交配得到的。第三个模拟群体是5个full-sib家系组成,每个家系包括50个子代,这50个子代是从繁育1000代的群体中随机挑选10个父本和10个母本交配得到的。第一、第二模拟群体只考虑加性遗传效应,第三个模拟群体不但考虑了加性遗传效应,还考虑了显性效应。
2b-RAD实验:349个扇贝个体,3个双亲用于2b-RAD测序和分型。2b-RAD建库包括标准文库和选择性碱基文库(reduced tag representation, RTR)文库。记录所有样品与生长相关的特征,包括长度、宽度和高度。
交叉验证:所有样品分成5个子集,4个子集(80%)用于估计分子标记效应,1个子集(20%)用于验证。
统计模型:BLUP、G-BLUP、Bayes(Bayes A和BayesB)、RR-BLUP、BL、LASSO ,共6种。
育种群体模拟:3个模拟群体,第一个模拟群体是从繁育1000代的群体中随机挑选100个父本和100个母本交配,每次交配得到20个子代G1,重复此过程得到G2。第二个模拟群体由20个full-sib家系组成,每个家系包括50个子代,这50个子代是从繁育1000代的群体中随机挑选10个父本和10个母本交配得到的。第三个模拟群体是5个full-sib家系组成,每个家系包括50个子代,这50个子代是从繁育1000代的群体中随机挑选10个父本和10个母本交配得到的。第一、第二模拟群体只考虑加性遗传效应,第三个模拟群体不但考虑了加性遗传效应,还考虑了显性效应。
2b-RAD实验:349个扇贝个体,3个双亲用于2b-RAD测序和分型。2b-RAD建库包括标准文库和选择性碱基文库(reduced tag representation, RTR)文库。记录所有样品与生长相关的特征,包括长度、宽度和高度。
交叉验证:所有样品分成5个子集,4个子集(80%)用于估计分子标记效应,1个子集(20%)用于验证。
统计模型:BLUP、G-BLUP、Bayes(Bayes A和BayesB)、RR-BLUP、BL、LASSO ,共6种。
研究结果
2b-RAD的预测准确性稍微低于用全部多态性位点获得的基因组育种值。
从RTR文库获得的少量分子标记来估计基因组育种值,与使用所有分子标记得到的基因组育种值相当,表明RTR可能是基因组选择的一种很有吸引力的方法。
6种基因组选择统计模型的预测准确性是变化的,这是由于遗传力、群体大小、群落结构等不同影响的。不过Bayes和BLUP的表现优于其他模型。
2b-RAD的预测准确性稍微低于用全部多态性位点获得的基因组育种值。
从RTR文库获得的少量分子标记来估计基因组育种值,与使用所有分子标记得到的基因组育种值相当,表明RTR可能是基因组选择的一种很有吸引力的方法。
6种基因组选择统计模型的预测准确性是变化的,这是由于遗传力、群体大小、群落结构等不同影响的。不过Bayes和BLUP的表现优于其他模型。
参考文献
Dou J, Li X, Fu Q, et al. Evaluation of the 2b-RAD method for genomic selection inscallop breeding[J]. Scientific reports,2016, 6. (IF:5.578)
应用6:细胞突变检测
研究背景:辐射对称动物与两侧对称动物共同组成真后生动物,研究表明两侧对称动物具有与成体干细胞相隔离的独立生殖干细胞系。细胞克隆实验证明,辐射对称动物下属的刺胞动物中的褐色水螅和大乳头水螅,存在体细胞与生殖细胞的隔离体系,但其他刺胞动物中仍缺乏相关证据来证明其是否也存在这种隔离体系。
研究内容:美国研究人员选用刺胞动物门的珊瑚虫(Orbicella faveolata)作为研究对象,利用2b-RAD技术对其不同世代体细胞、不同世代精细胞以及体细胞与精细胞之间的遗传水平差异进行研究,发现珊瑚虫也具有独立的生殖干细胞系,并可根据体细胞与生殖细胞之间的遗传差异情况对细胞传代数进行鉴定。
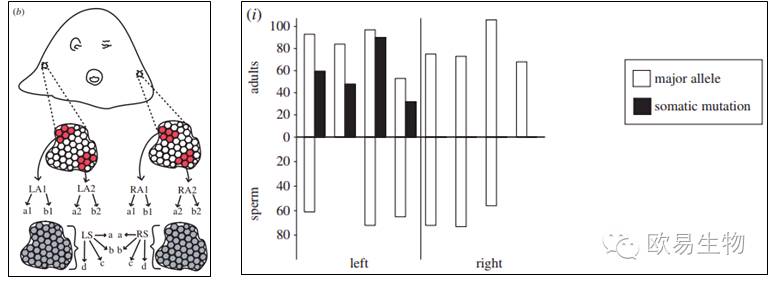
图1 实验材料取样模式图
图2 Colony B 中一个SNP的检测结果
研究策略
实验材料:2个珊瑚虫群体A和B,每个群体的取样方式相同,即从群体相对的两侧各取一块组织片段,分别收集精细胞和体细胞,每侧收集到的精细胞4个重复,体细胞4个重复(图1)。两个群体共取样32份全部进行2b-RAD建库。
文库构建:按照2b-RAD文库构建流程,使用Bcg I和Alf I两种IIB型内切酶进行构建。
数据分析:在鉴定体细胞突变时,每一侧的四份重复样品分型完全一致,但两侧之间的分型不同,认为是突变位点。
实验材料:2个珊瑚虫群体A和B,每个群体的取样方式相同,即从群体相对的两侧各取一块组织片段,分别收集精细胞和体细胞,每侧收集到的精细胞4个重复,体细胞4个重复(图1)。两个群体共取样32份全部进行2b-RAD建库。
文库构建:按照2b-RAD文库构建流程,使用Bcg I和Alf I两种IIB型内切酶进行构建。
数据分析:在鉴定体细胞突变时,每一侧的四份重复样品分型完全一致,但两侧之间的分型不同,认为是突变位点。
研究结果
体细胞突变的检测:两个群体共检测出9个体细胞突变位点,其中群体 A 4个,群体B 5个。
精细胞突变检测:体细胞中检测出的9个突变位点(图2展示了其中一个),但在精细胞之间没有被检测出,表明珊瑚虫拥有一个完全独立的生殖干细胞系,体细胞突变不会遗传给通过有性生殖方式产生的下一代,却能通过无性生殖(出芽生殖)的方式向下一代传递。另外,也没有发现有精细胞存在特异的突变位点。
体细胞突变的检测:两个群体共检测出9个体细胞突变位点,其中群体 A 4个,群体B 5个。
精细胞突变检测:体细胞中检测出的9个突变位点(图2展示了其中一个),但在精细胞之间没有被检测出,表明珊瑚虫拥有一个完全独立的生殖干细胞系,体细胞突变不会遗传给通过有性生殖方式产生的下一代,却能通过无性生殖(出芽生殖)的方式向下一代传递。另外,也没有发现有精细胞存在特异的突变位点。
参考文献
Barfield S, Aglyamova G V, Matz M V.Evolutionary origins of germline segregation in Metazoa: evidence for a germstem cell lineage in the coral Orbicellafaveolata (Cnidaria, Anthozoa)[C]. Proc. R. Soc. B. The Royal Society, 2016, 283(1822):20152128. (IF:5.051) 返回搜狐,查看更多
责任编辑: